均值和协方差函数#
import arviz as az
import matplotlib.pyplot as plt
import numpy as np
import pymc as pm
import pytensor.tensor as pt
%config InlineBackend.figure_format = "retina"
WARNING (pytensor.tensor.blas): Using NumPy C-API based implementation for BLAS functions.
RANDOM_SEED = 8927
rng = np.random.default_rng(RANDOM_SEED)
az.style.use("arviz-darkgrid")
plt.rcParams["figure.figsize"] = (10, 4)
PyMC 中提供了大量均值和协方差函数。定义自定义的均值和协方差函数相对容易。由于 PyMC 使用 PyTensor,因此用户不需要定义它们的梯度。
均值函数#
以下均值函数在 PyMC 中可用。
所有遵循相似的使用模式。首先,指定均值函数。然后可以在某些输入上进行评估。前两个均值函数非常简单。无论输入如何,gp.mean.Zero 返回一个与输入值数量相同长度的零向量。
零#
zero_func = pm.gp.mean.Zero()
X = np.linspace(0, 1, 5)[:, None]
print(zero_func(X).eval())
[0. 0. 0. 0. 0.]
PyMC中所有GP实现的默认均值函数是零。
常量#
gp.mean.Constant 返回一个值为提供的向量。
const_func = pm.gp.mean.Constant(25.2)
print(const_func(X).eval())
[25.2 25.2 25.2 25.2 25.2]
只要形状与它将接收的输入匹配,gp.mean.Constant 也可以接受 PyTensor 张量或 PyMC 随机变量的向量。
const_func_vec = pm.gp.mean.Constant(pt.ones(5))
print(const_func_vec(X).eval())
[1. 1. 1. 1. 1.]
线性#
gp.mean.Linear 是一个接受系数矩阵和截距向量(或在一维情况下接受斜率和标量截距)作为输入的函数。
beta = rng.normal(size=3)
b = 0.0
lin_func = pm.gp.mean.Linear(coeffs=beta, intercept=b)
X = rng.normal(size=(5, 3))
print(lin_func(X).eval())
[ 1.03424803 -2.25903687 0.78030931 0.9880038 -3.45565466]
定义自定义均值函数#
要定义一个自定义的均值函数,可以继承 gp.mean.Mean,并提供 __call__ 和 __init__ 方法。例如,Constant 均值函数的代码如下
import theano.tensor as tt
class Constant(pm.gp.mean.Mean):
def __init__(self, c=0):
Mean.__init__(self)
self.c = c
def __call__(self, X):
return tt.alloc(1.0, X.shape[0]) * self.c
请记住,必须使用 PyTensor 而不是 NumPy。
协方差函数#
PyMC 包含了一系列更丰富的 内置 协方差 函数。 以下展示了从具有给定协方差函数的 GP 先验中抽取的函数,并演示了如何使用 Python 运算符以直接的方式构建复合协方差函数。 我们的目标是使我们的 API 尽可能地遵循核代数(参见 Rasmussen 和 Williams [2006] 的第 4 章)。 请参阅主要文档页面以了解它们在 PyMC 中的使用概述。
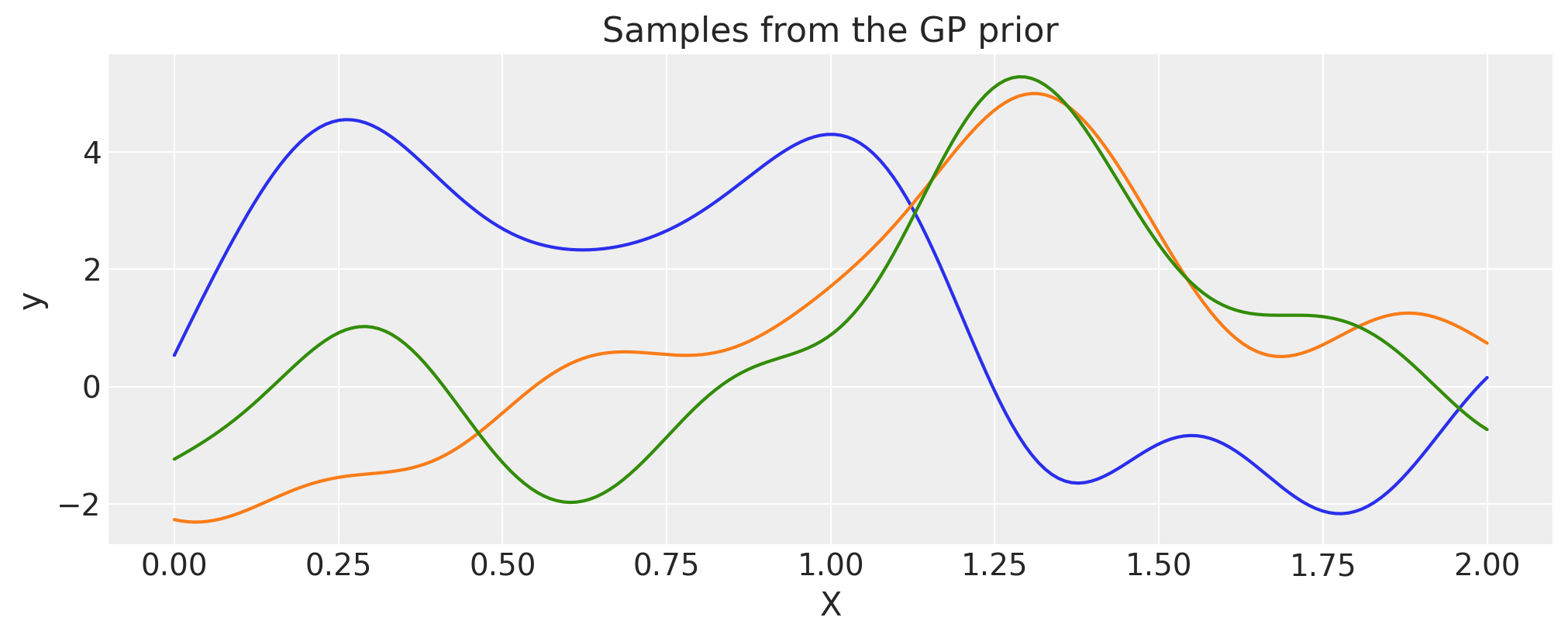
指数二次方#
lengthscale = 0.2
eta = 2.0
cov = eta**2 * pm.gp.cov.ExpQuad(1, lengthscale)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(
pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=K.shape[0]), draws=3, random_seed=rng
).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
二维(及更高维)输入#
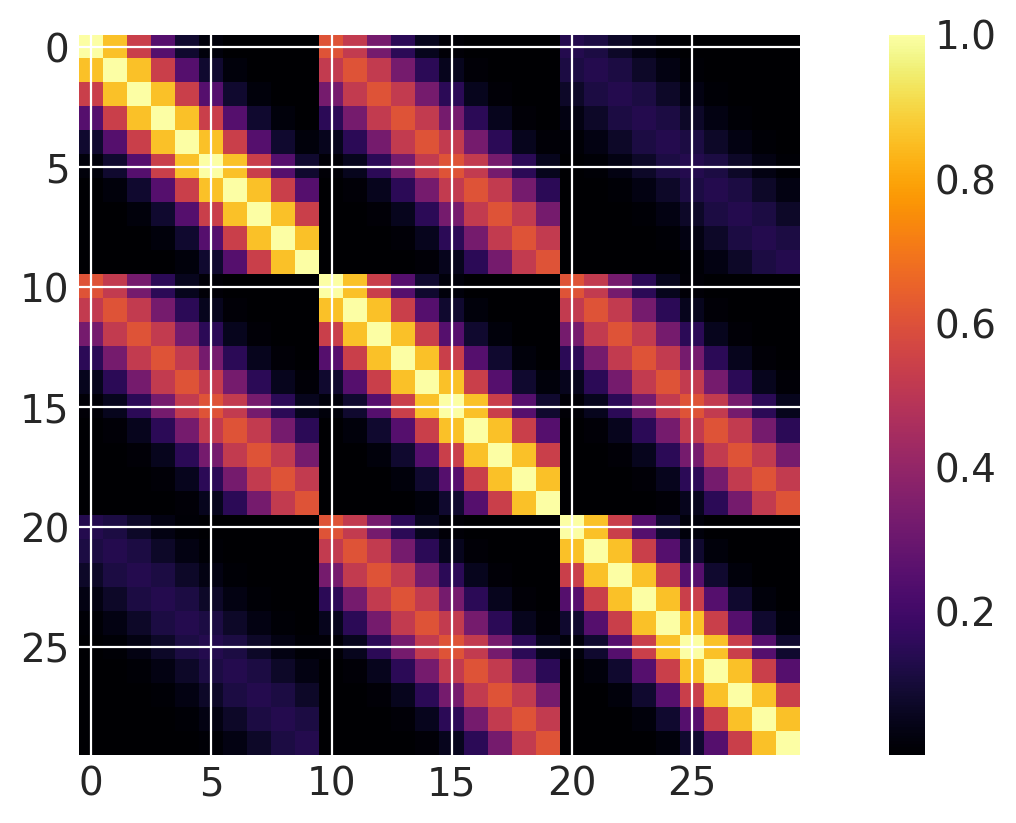
两个维度均激活#
定义具有高维输入的核很容易。请注意,ls(长度尺度)参数是一个长度为2的数组。PyMC随机变量的列表可以用于自动相关性确定(ARD)。
x1 = np.linspace(0, 1, 10)
x2 = np.arange(1, 4)
# Cartesian product
X2 = np.dstack(np.meshgrid(x1, x2)).reshape(-1, 2)
ls = np.array([0.2, 1.0])
cov = pm.gp.cov.ExpQuad(input_dim=2, ls=ls)
m = plt.imshow(cov(X2).eval(), cmap="inferno", interpolation="none")
plt.colorbar(m);
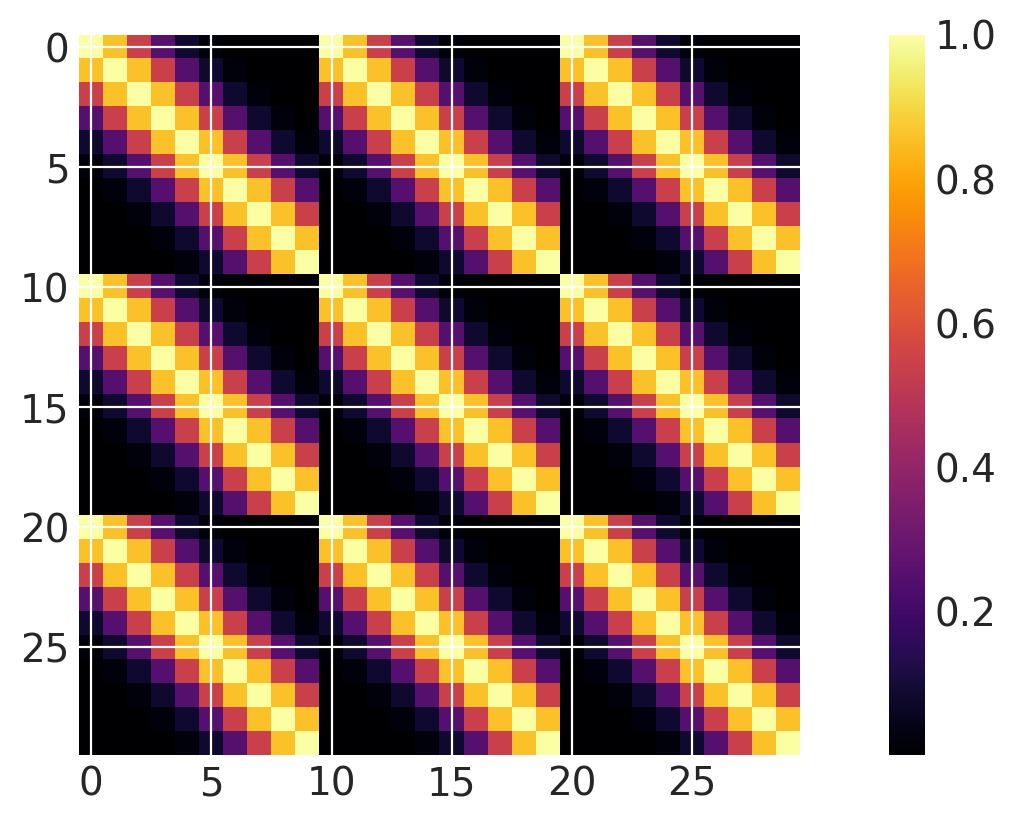
一维活动#
ls = 0.2
cov = pm.gp.cov.ExpQuad(input_dim=2, ls=ls, active_dims=[0])
m = plt.imshow(cov(X2).eval(), cmap="inferno", interpolation="none")
plt.colorbar(m);
不同维度上协方差乘积#
请注意,这相当于使用一个二维的 ExpQuad,并为每个维度使用单独的长度尺度参数。
ls1 = 0.2
ls2 = 1.0
cov1 = pm.gp.cov.ExpQuad(2, ls1, active_dims=[0])
cov2 = pm.gp.cov.ExpQuad(2, ls2, active_dims=[1])
cov = cov1 * cov2
m = plt.imshow(cov(X2).eval(), cmap="inferno", interpolation="none")
plt.colorbar(m);

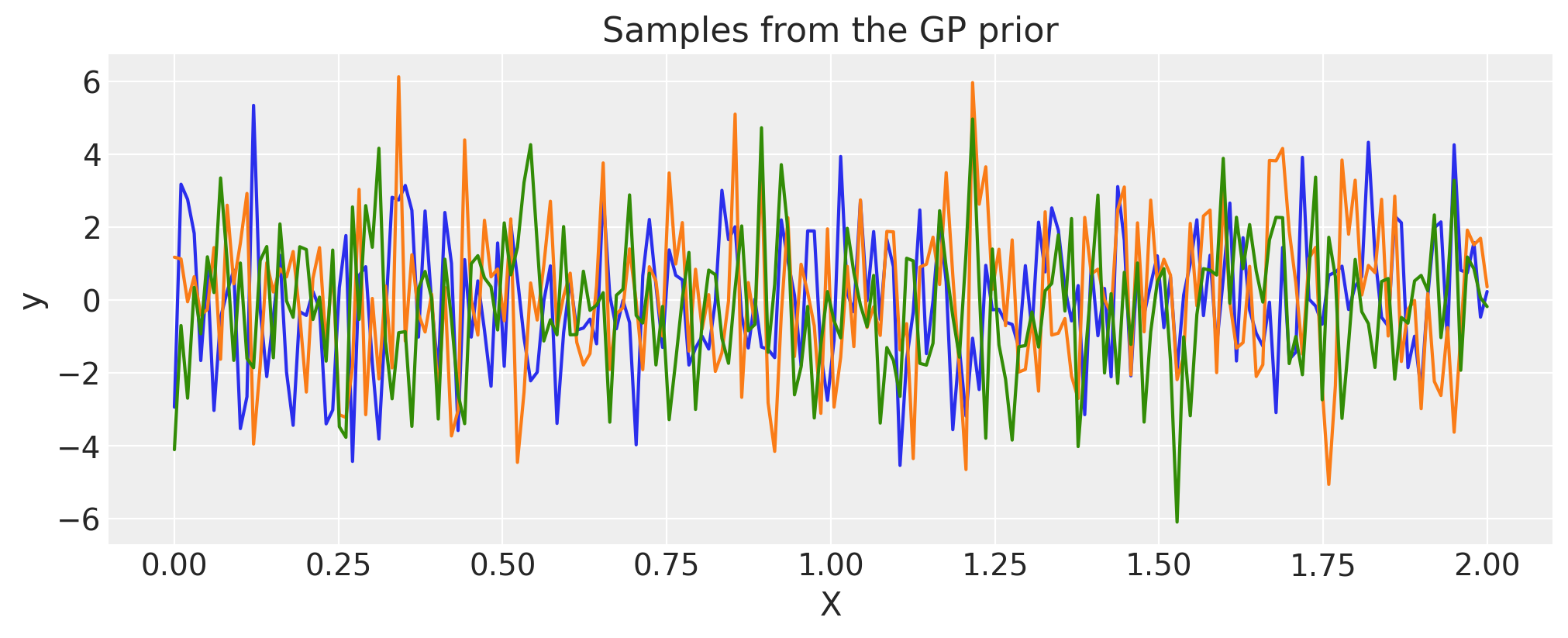
白噪声#
sigma = 2.0
cov = pm.gp.cov.WhiteNoise(sigma)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
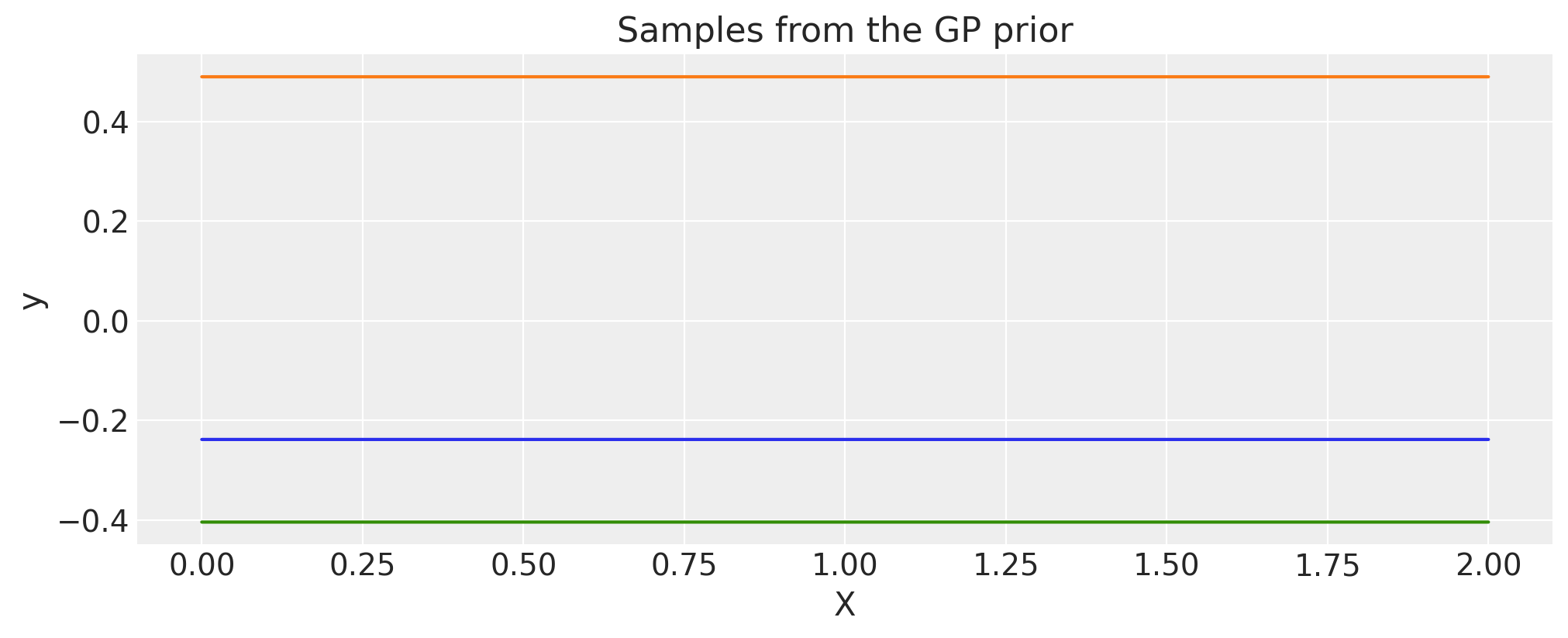
常量#
c = 2.0
cov = pm.gp.cov.Constant(c)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
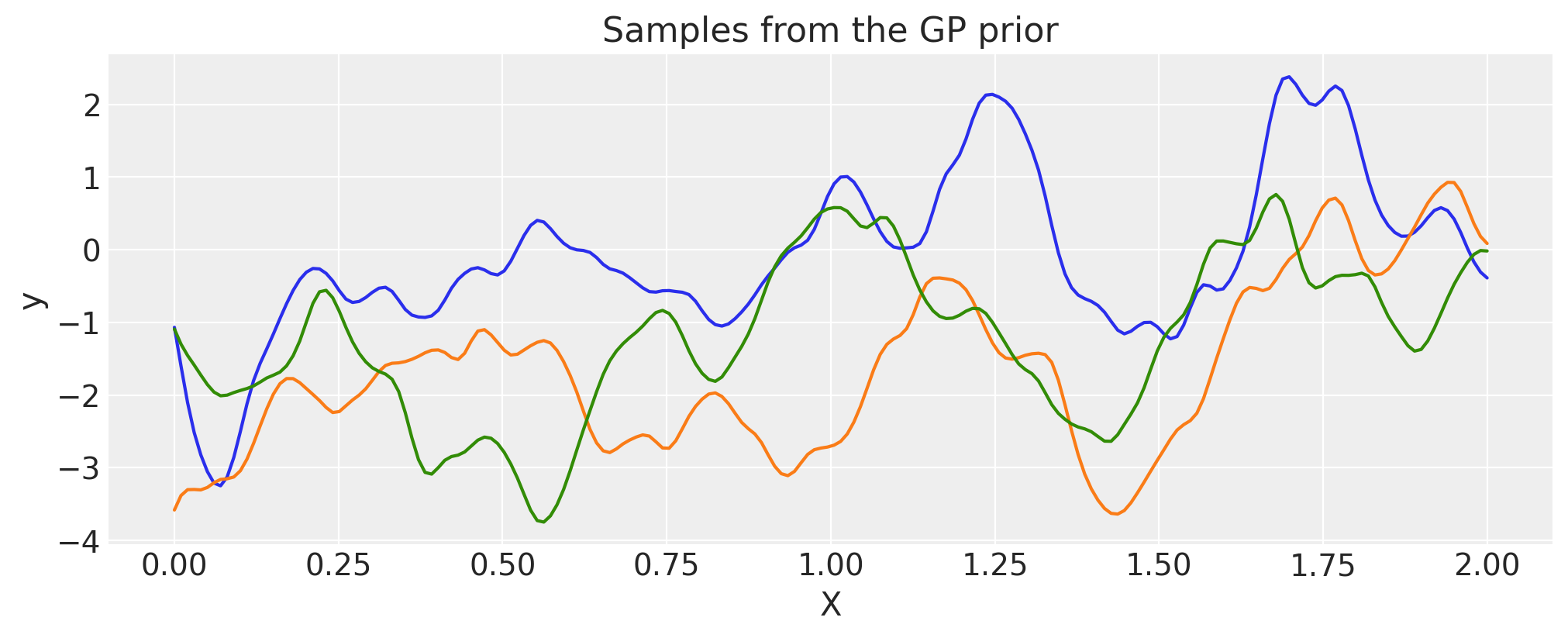
有理二次#
alpha = 0.1
ls = 0.2
tau = 2.0
cov = tau * pm.gp.cov.RatQuad(1, ls, alpha)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
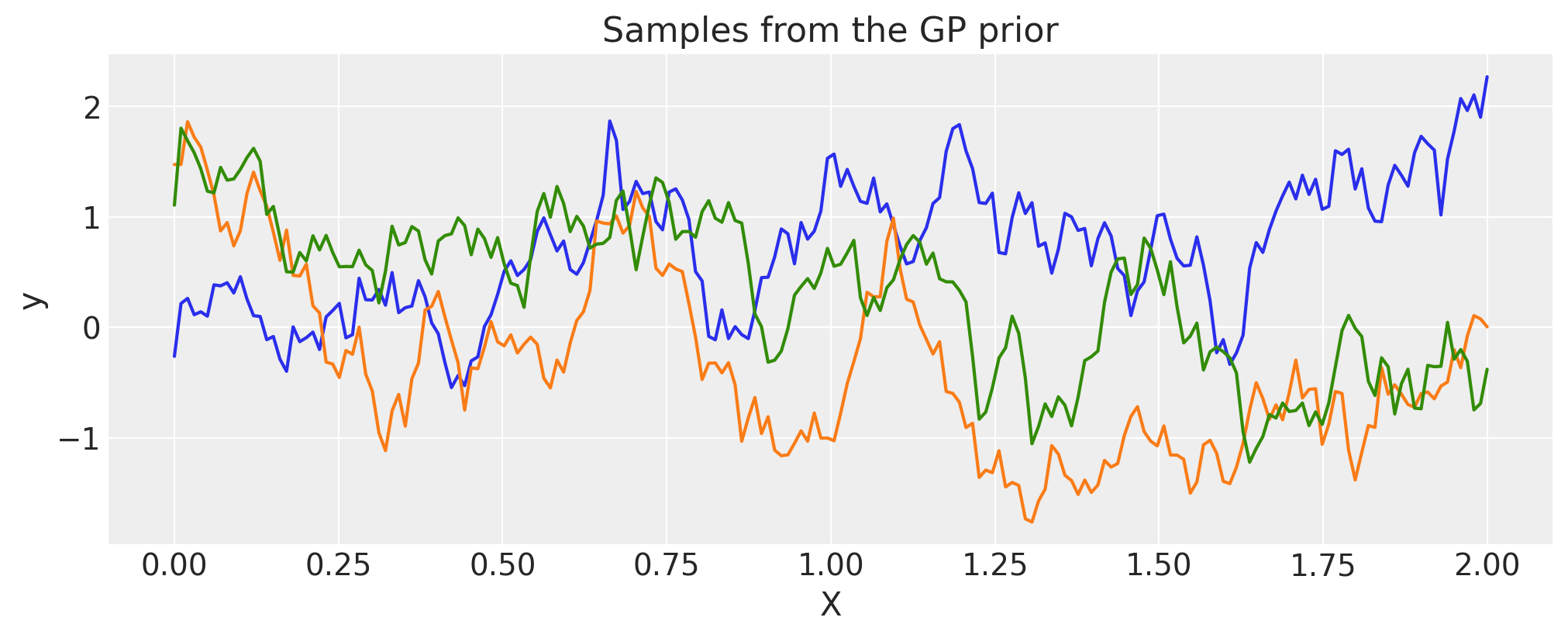
指数#
inverse_lengthscale = 5
cov = pm.gp.cov.Exponential(1, ls_inv=inverse_lengthscale)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
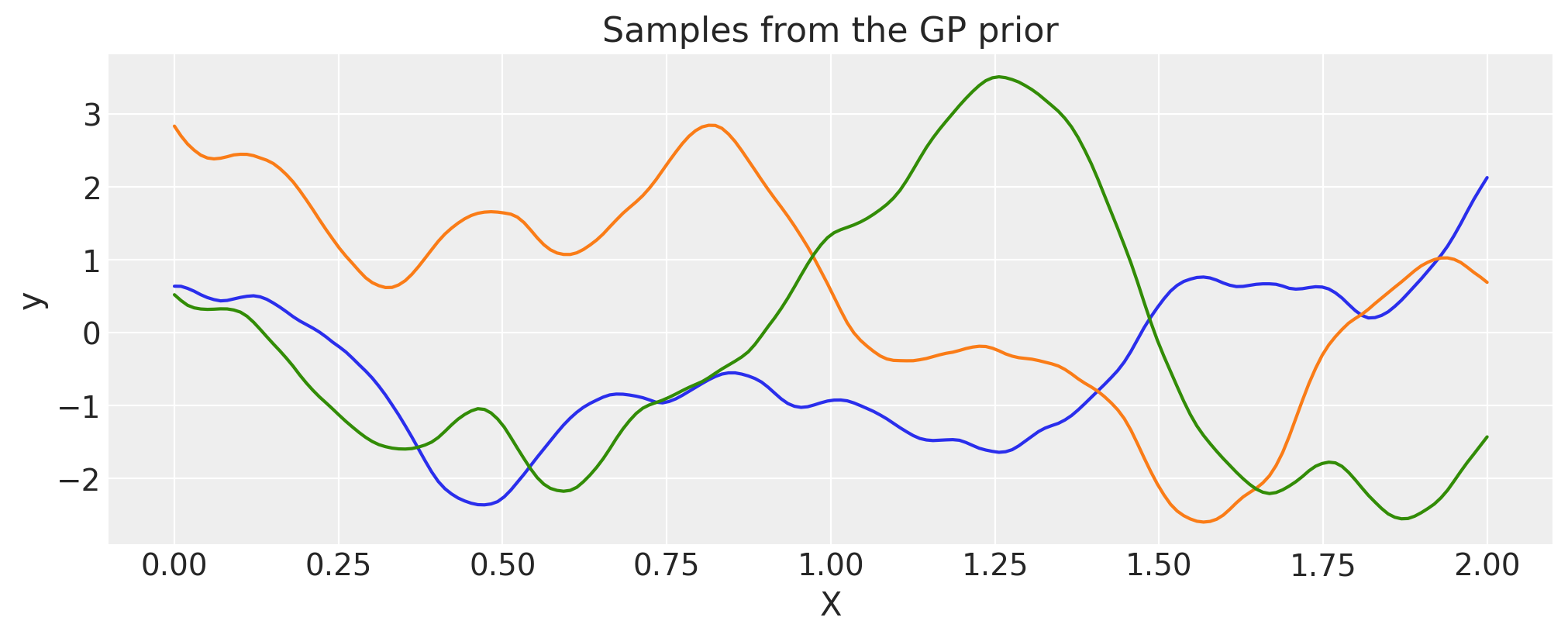
Matern 5/2#
ls = 0.2
tau = 2.0
cov = tau * pm.gp.cov.Matern52(1, ls)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
Matern 3/2#
ls = 0.2
tau = 2.0
cov = tau * pm.gp.cov.Matern32(1, ls)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
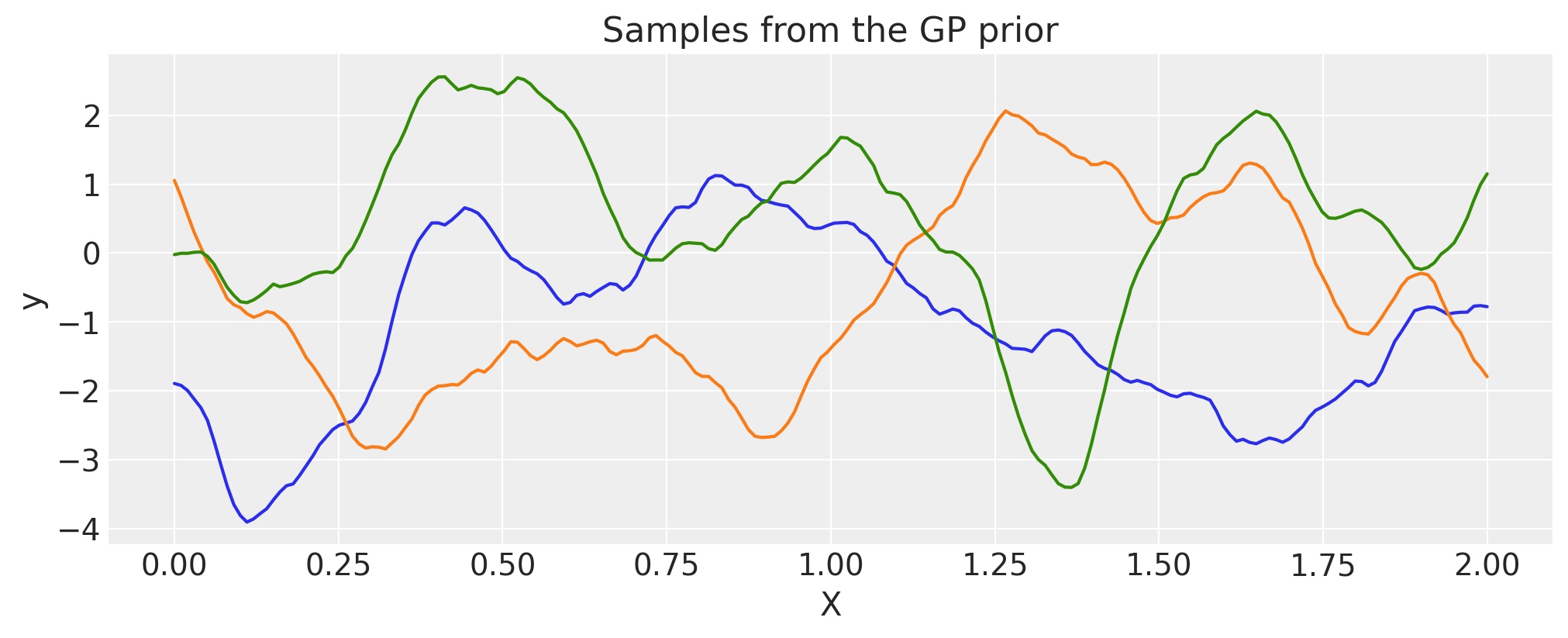
Matern 1/2#
ls = 0.2
tau = 2.0
cov = tau * pm.gp.cov.Matern12(1, ls)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
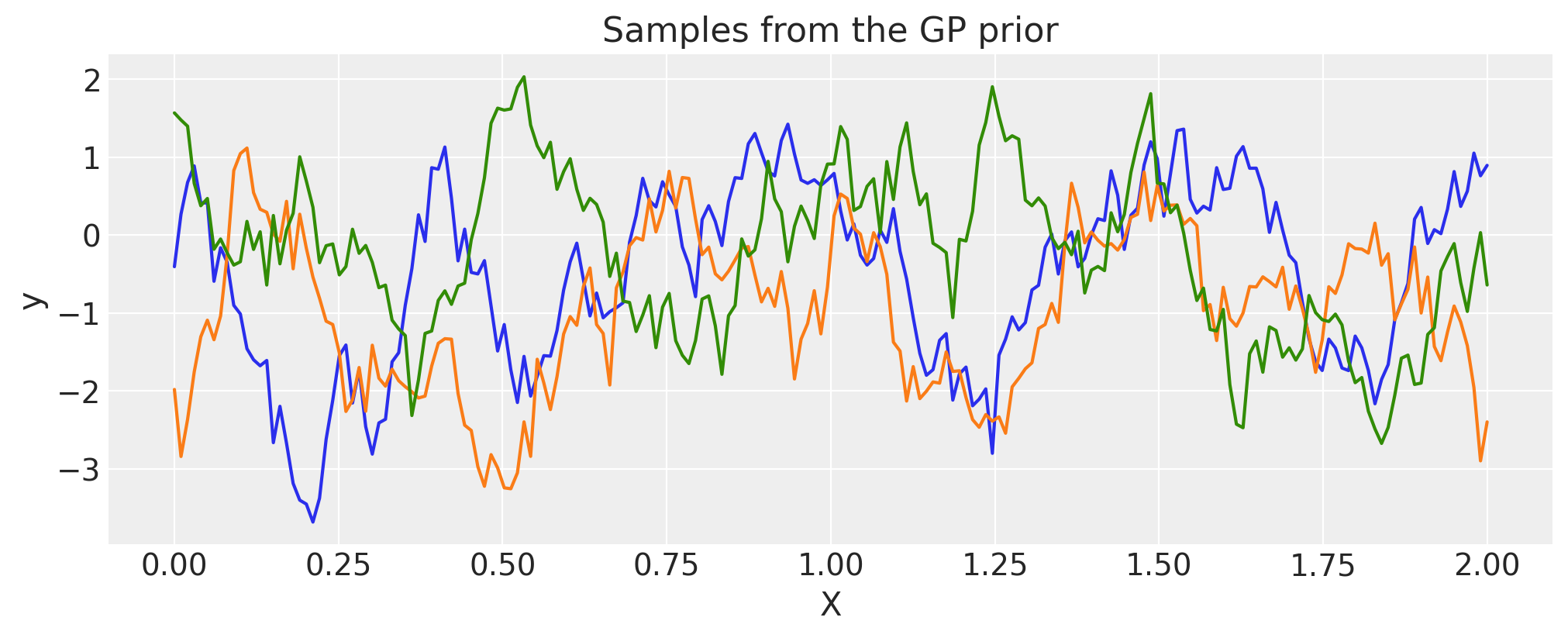
余弦#
period = 0.5
cov = pm.gp.cov.Cosine(1, period)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-4)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
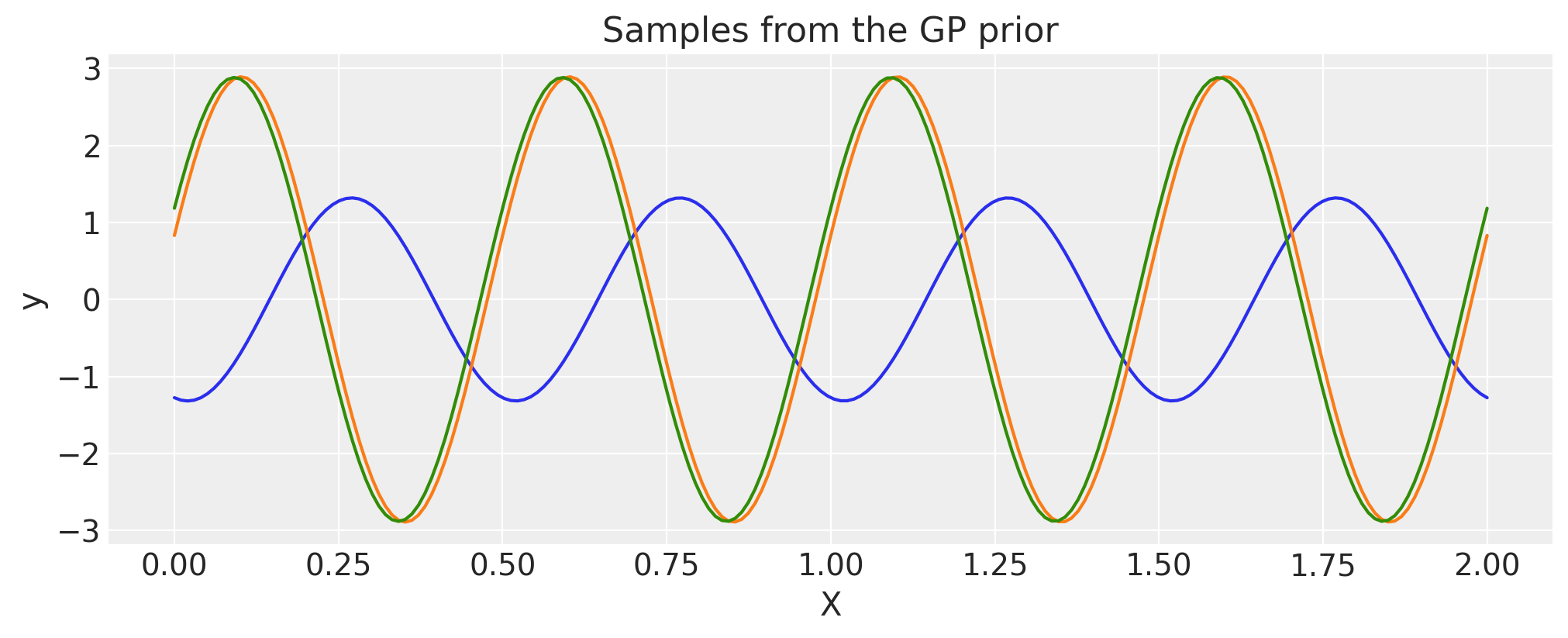
线性#
c = 1.0
tau = 2.0
cov = tau * pm.gp.cov.Linear(1, c)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
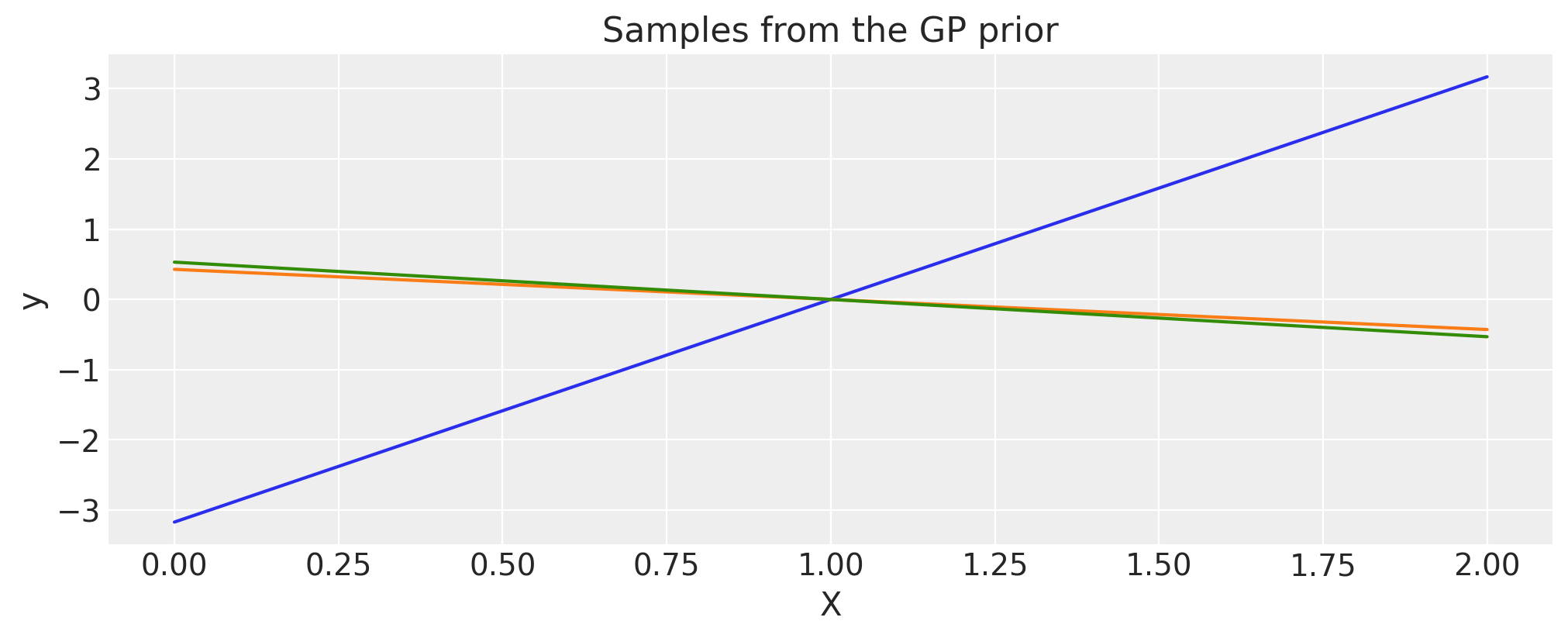
多项式#
c = 1.0
d = 3
offset = 1.0
tau = 0.1
cov = tau * pm.gp.cov.Polynomial(1, c=c, d=d, offset=offset)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
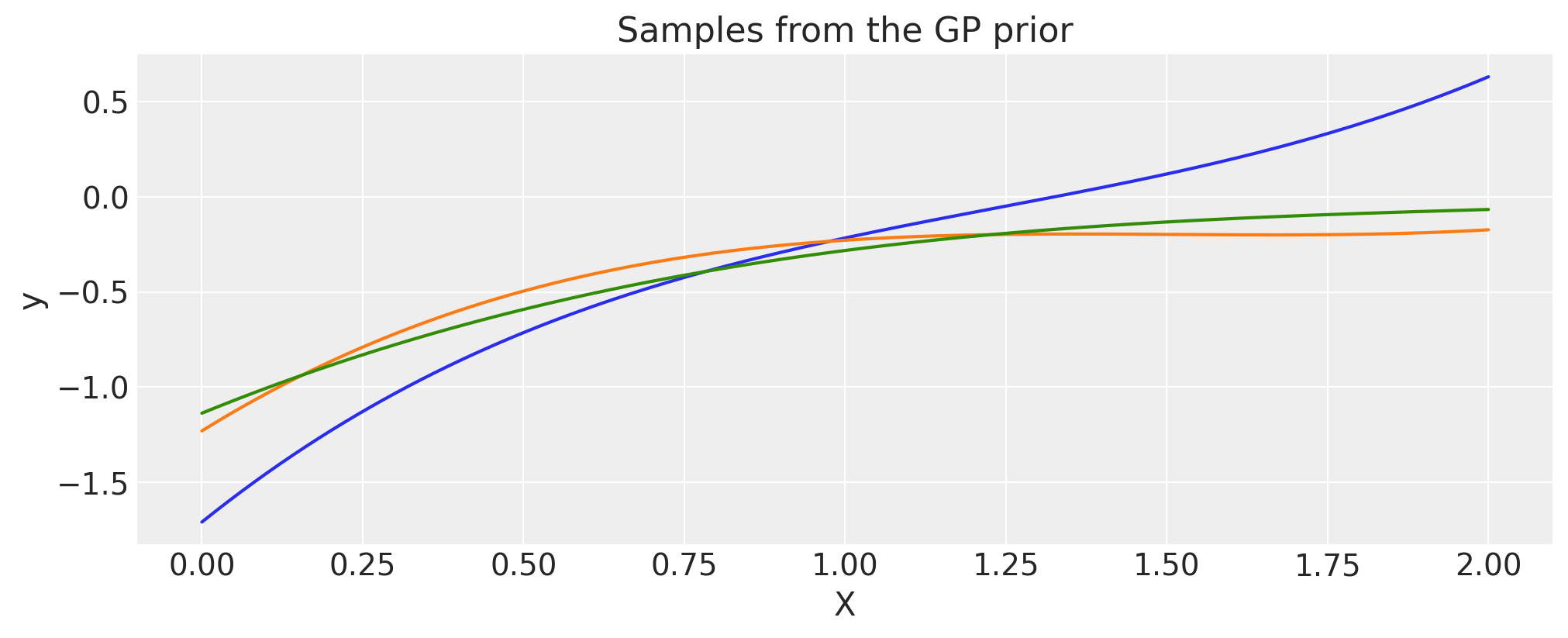
使用预计算协方差矩阵进行乘法#
协方差函数 cov 可以与 numpy 矩阵 K_cos 相乘,只要形状合适即可。
# first evaluate a covariance function into a matrix
period = 0.2
cov_cos = pm.gp.cov.Cosine(1, period)
K_cos = cov_cos(X).eval()
# now multiply it with a covariance *function*
cov = pm.gp.cov.Matern32(1, 0.5) * K_cos
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
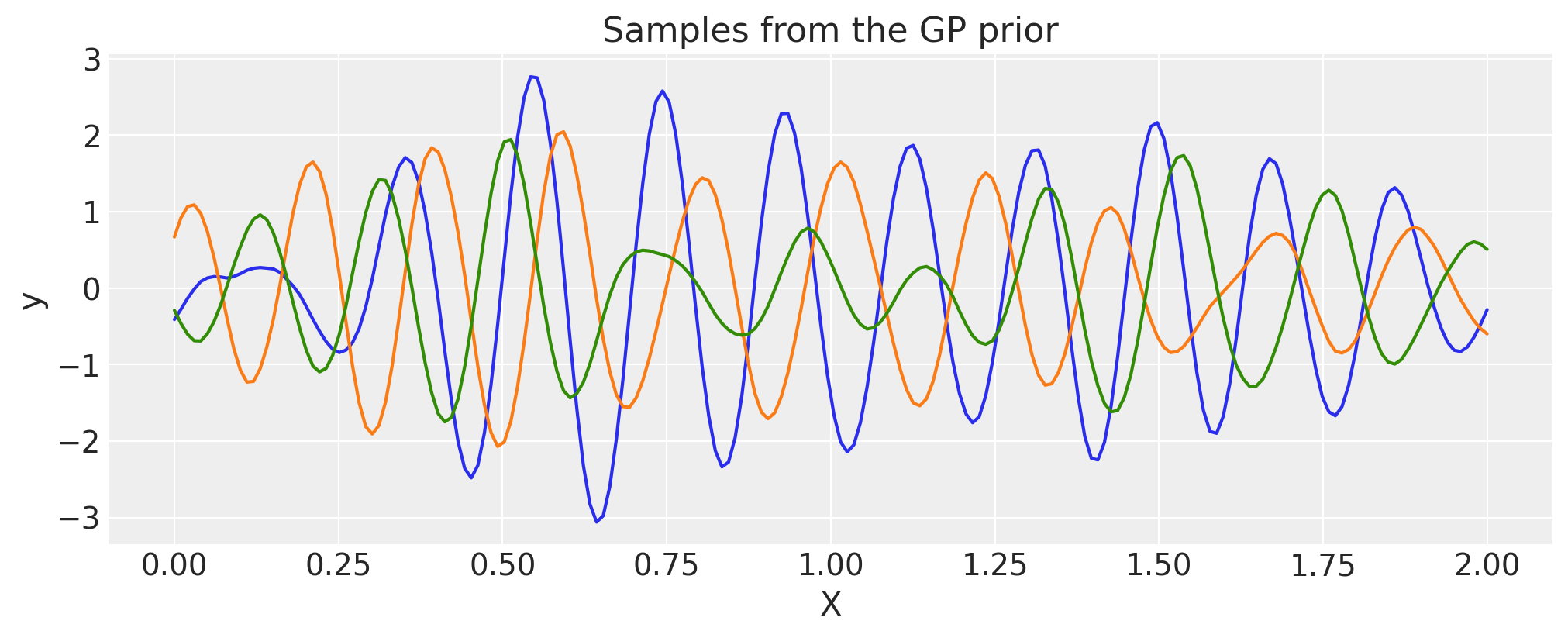
对输入应用任意变形函数#
如果 \(k(x, x')\) 是一个有效的协方差函数,那么 \(k(w(x), w(x'))\) 也是一个有效的协方差函数。
扭曲函数的第一个参数必须是输入 X。其余参数可以是任何其他内容,包括随机变量。
def warp_func(x, a, b, c):
return 1.0 + x + (a * pt.tanh(b * (x - c)))
a = 1.0
b = 5.0
c = 1.0
cov_exp = pm.gp.cov.ExpQuad(1, 0.2)
cov = pm.gp.cov.WarpedInput(1, warp_func=warp_func, args=(a, b, c), cov_func=cov_exp)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 400)[:, None]
wf = warp_func(X.flatten(), a, b, c).eval()
plt.plot(X, wf)
plt.xlabel("X")
plt.ylabel("warp_func(X)")
plt.title("The warping function used")
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
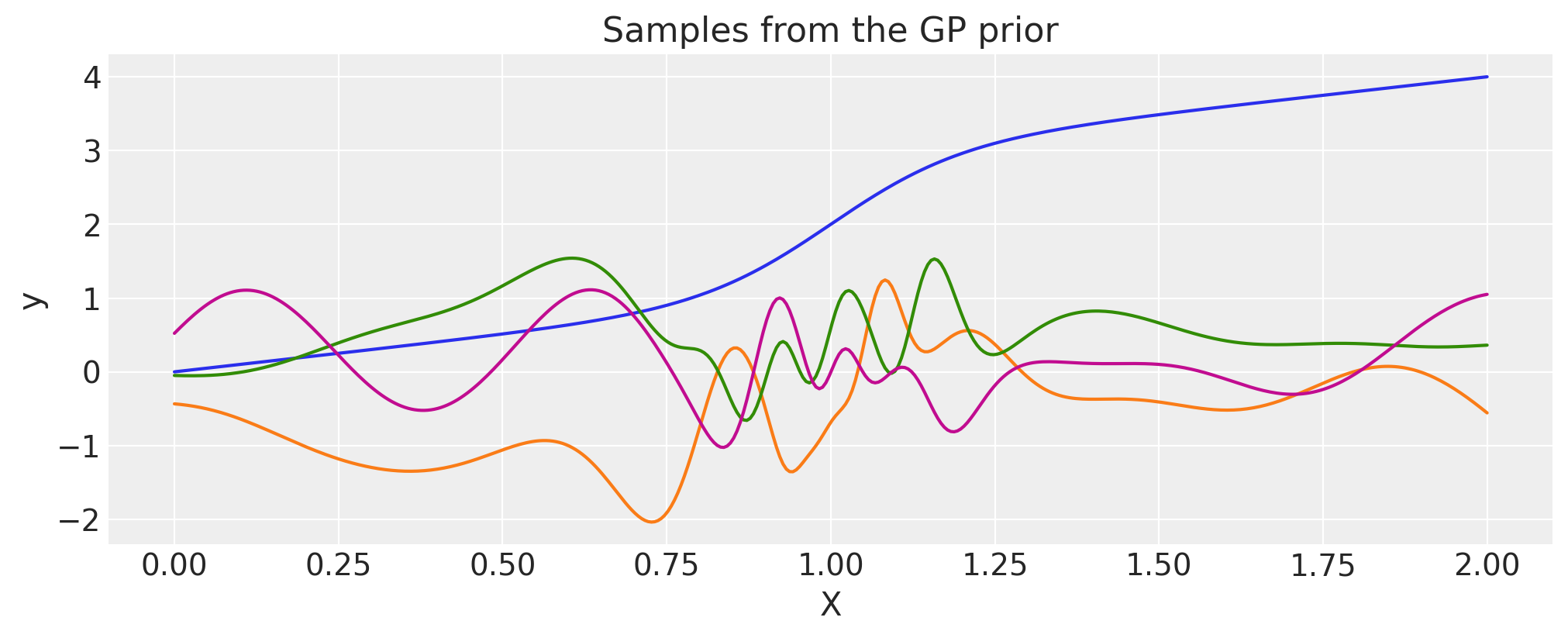
使用WarpedInput构建Periodic#
The WarpedInput 核函数可以用来创建 Periodic 协方差。这种协方差模型用于描述周期性函数,但不是精确的正弦波(如 Cosine 核函数那样)。
周期核由以下公式给出
其中 T 是周期,\(\ell\) 是长度尺度。 它可以通过使用函数 \(\mathbf{u}(x) = (\sin(2\pi x \frac{1}{T})\,, \cos(2 \pi x \frac{1}{T}))\) 对 ExpQuad 核的输入进行变形来推导。 这里我们使用 WarpedInput 核来构建它。
输入 X,在本页顶部定义,长度为2“秒”。我们使用一个周期为 \(0.5\),这意味着从此GP先验中绘制的函数将在2秒内重复4次。
def mapping(x, T):
c = 2.0 * np.pi * (1.0 / T)
u = pt.concatenate((pt.sin(c * x), pt.cos(c * x)), 1)
return u
T = 0.6
ls = 0.4
# note that the input of the covariance function taking
# the inputs is 2 dimensional
cov_exp = pm.gp.cov.ExpQuad(2, ls)
cov = pm.gp.cov.WarpedInput(1, cov_func=cov_exp, warp_func=mapping, args=(T,))
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
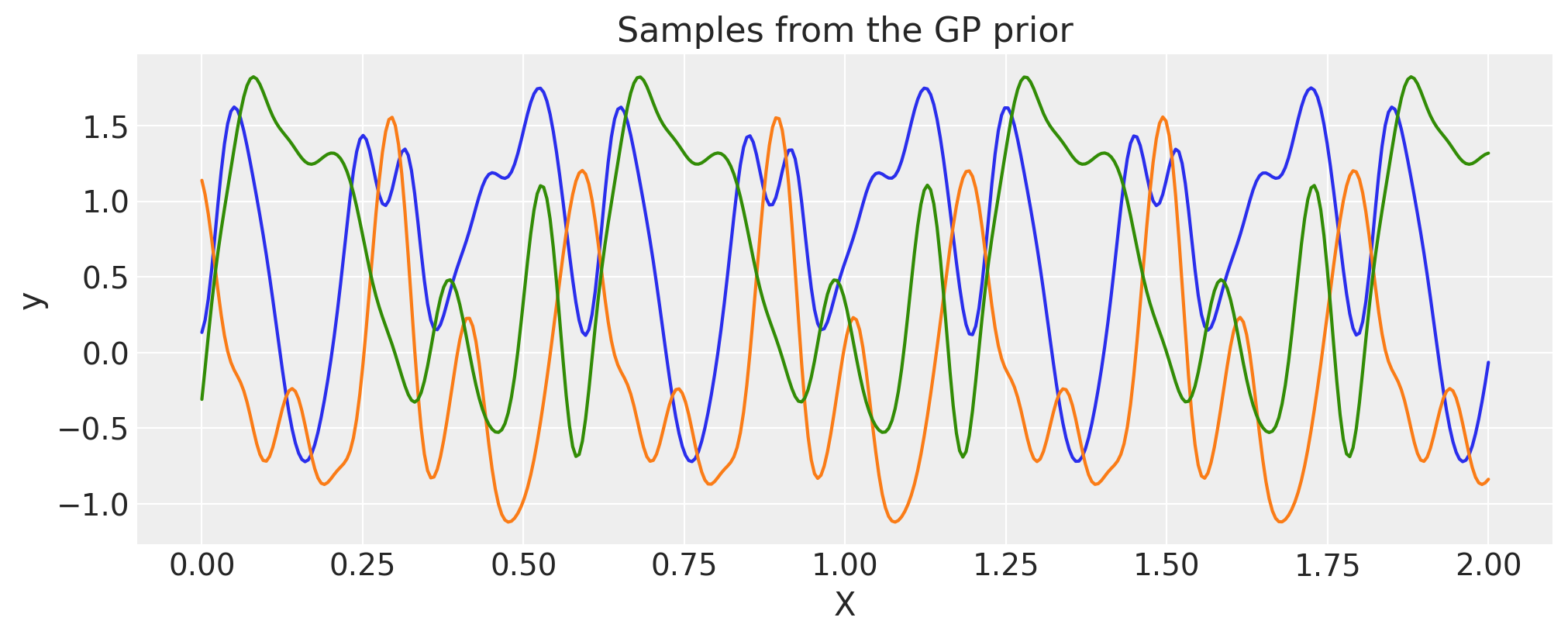
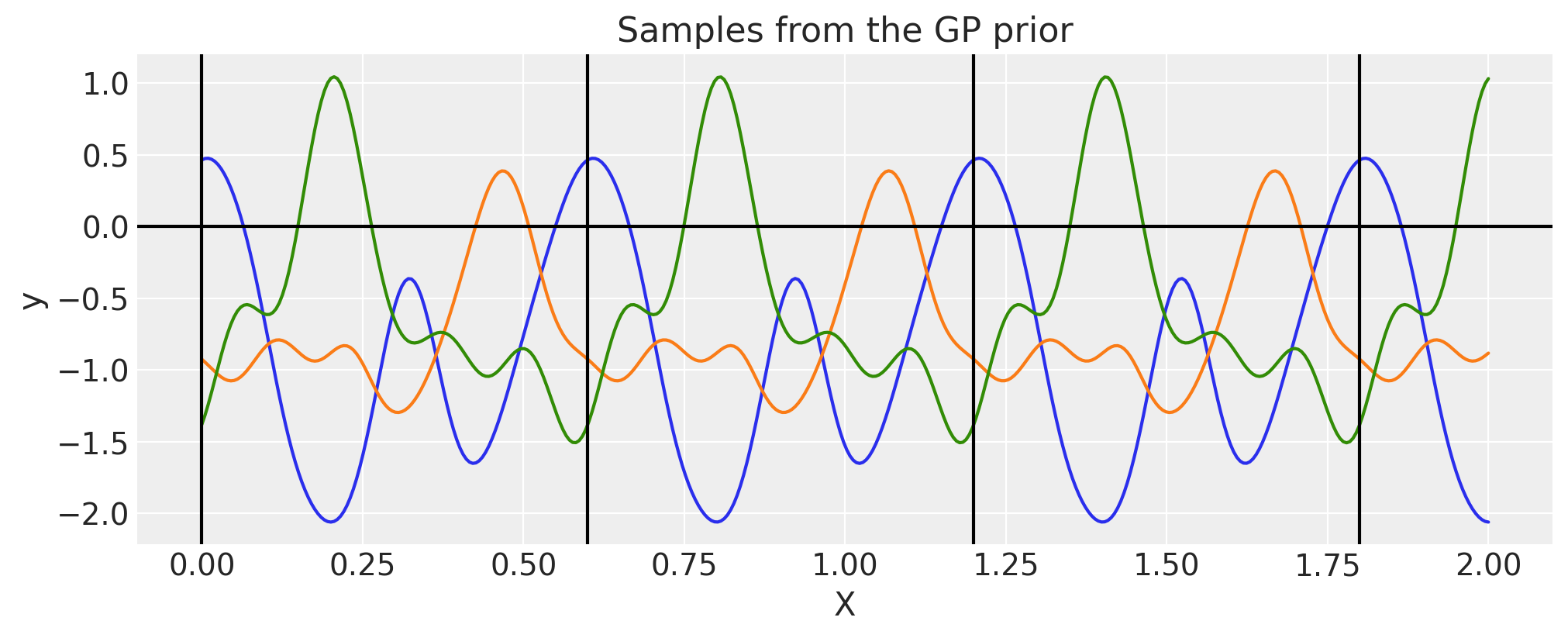
周期性#
不需要每次都以这种方式构建周期性协方差。这种协方差函数的一个更高效的实现已经内置了。
period = 0.6
ls = 0.4
cov = pm.gp.cov.Periodic(1, period=period, ls=ls)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
for p in np.arange(0, 2, period):
plt.axvline(p, color="black")
plt.axhline(0, color="black")
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
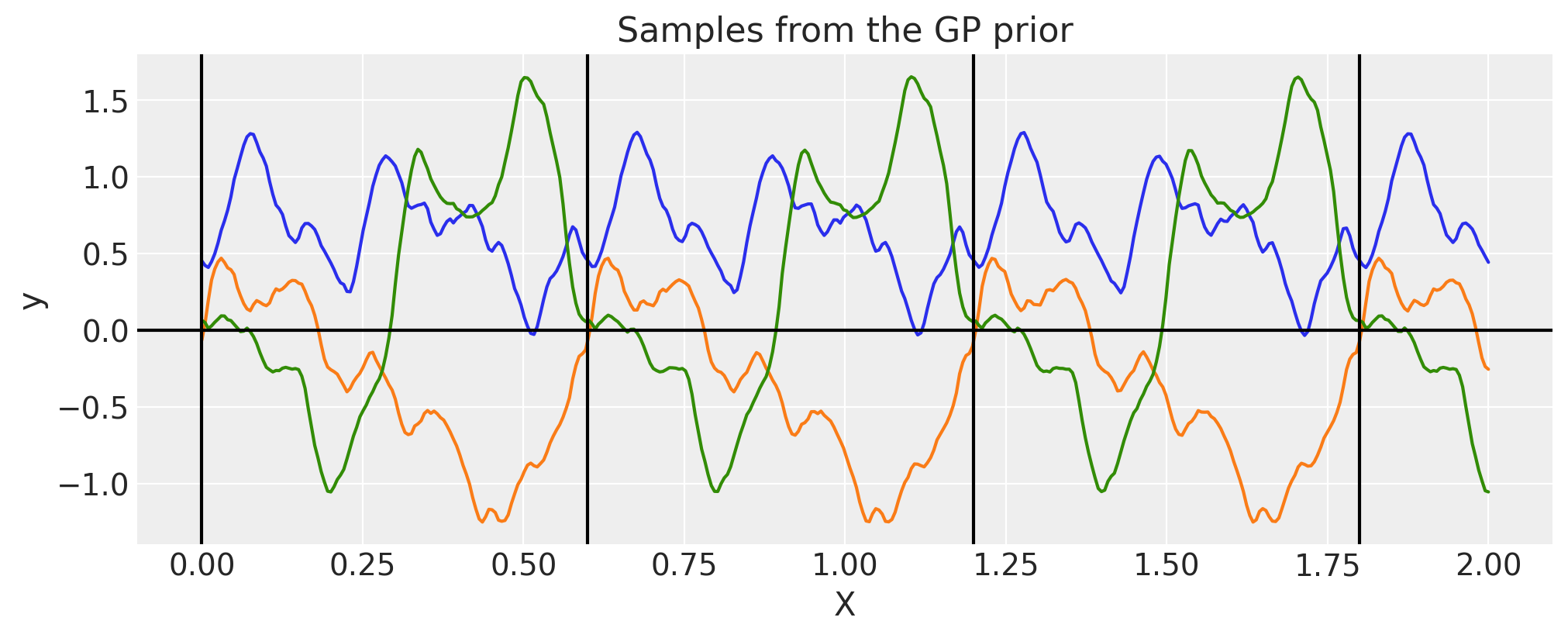
循环#
圆形核与周期性核相似,但具有一个额外的干扰参数 \(\tau\)
在Padonou 和 Roustant [2015]中,Weinland 函数被用于解决问题,并确保在圆形域(不仅仅是)上的正定核。
其中 \(c\) 是 \(t\) 的最大值,而 \(\tau\ge 4\) 是某个正数
用于计算圆上测地距离(弧长)的内核本身看起来像
简而言之,你可以认为
\(t\) 是时间,它从 \(0\) 运行到 \(24\),然后回到 \(0\)
\(c\) 是任意时间戳之间的最大距离,这里将是 \(12\)
\(\tau\) 控制相关性强度,较大的 \(\tau\) 会导致更不光滑的函数
period = 0.6
tau = 4
cov = pm.gp.cov.Circular(1, period=period, tau=tau)
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
for p in np.arange(0, 2, period):
plt.axvline(p, color="black")
plt.axhline(0, color="black")
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
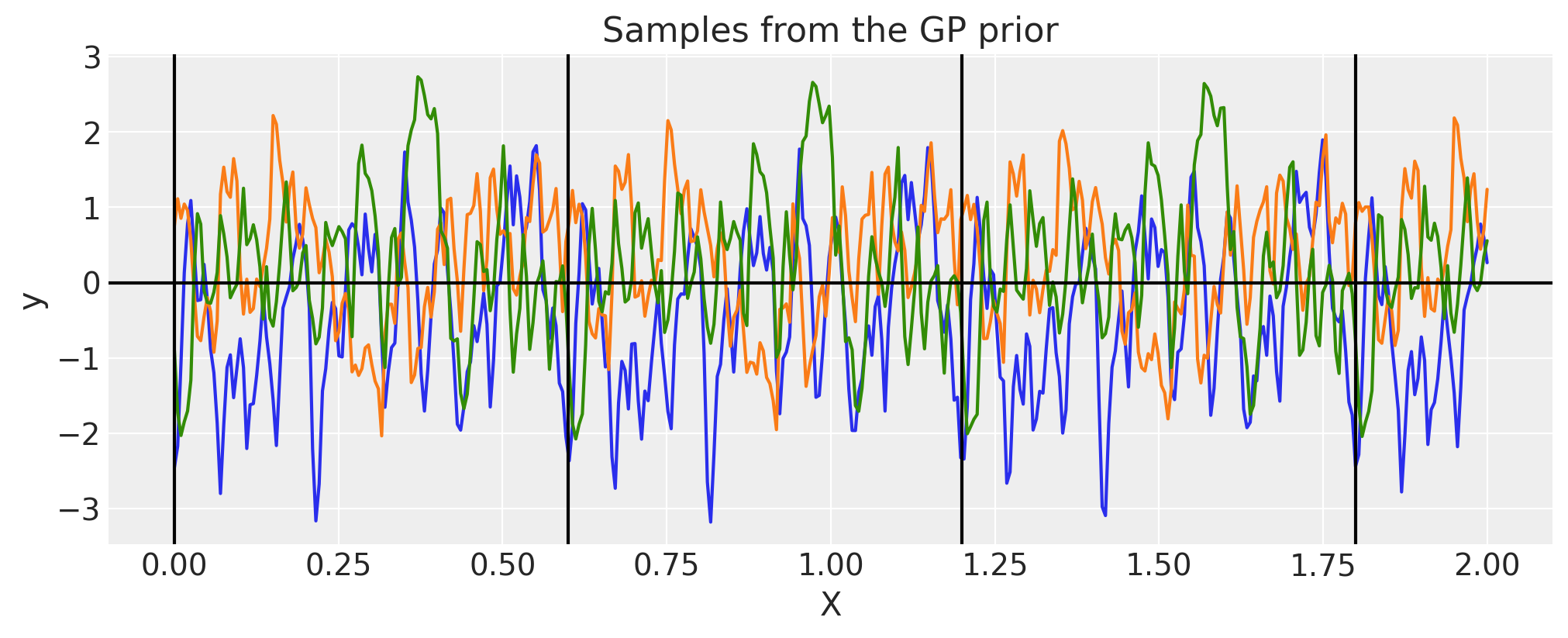
我们可以看到\(\tau\)的效果,它增加了更多的非平滑模式
period = 0.6
tau = 40
cov = pm.gp.cov.Circular(1, period=period, tau=tau)
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
for p in np.arange(0, 2, period):
plt.axvline(p, color="black")
plt.axhline(0, color="black")
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
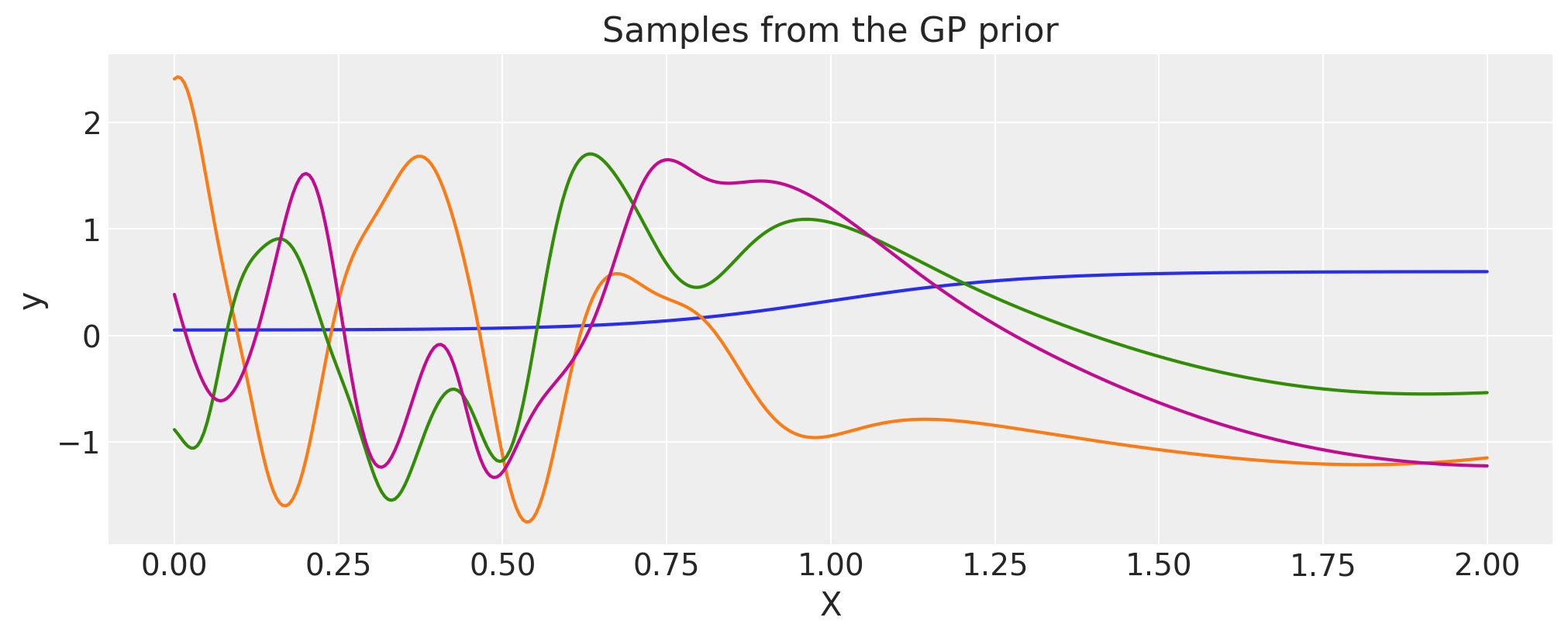
吉布斯#
吉布斯协方差函数对长度尺度应用了一个正定扭曲函数。与WarpedInput类似,长度尺度扭曲函数可以通过参数指定,这些参数可以是固定值或随机变量。
def tanh_func(x, ls1, ls2, w, x0):
"""
ls1: left saturation value
ls2: right saturation value
w: transition width
x0: transition location.
"""
return (ls1 + ls2) / 2.0 - (ls1 - ls2) / 2.0 * pt.tanh((x - x0) / w)
ls1 = 0.05
ls2 = 0.6
w = 0.3
x0 = 1.0
cov = pm.gp.cov.Gibbs(1, tanh_func, args=(ls1, ls2, w, x0))
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
wf = tanh_func(X, ls1, ls2, w, x0).eval()
plt.plot(X, wf)
plt.ylabel("lengthscale")
plt.xlabel("X")
plt.title("Lengthscale as a function of X")
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
缩放协方差#
可以通过将某个基本核函数乘以一个非负函数 \(\phi(x)\) 来构造一个新的核函数或协方差函数。
这对于指定协方差函数在其定义域内振幅变化的情况非常有用。
def logistic(x, a, x0, c, d):
# a is the slope, x0 is the location
return d * pm.math.invlogit(a * (x - x0)) + c
a = 2.0
x0 = 5.0
c = 0.1
d = 2.0
cov_base = pm.gp.cov.ExpQuad(1, 0.2)
cov = pm.gp.cov.ScaledCov(1, scaling_func=logistic, args=(a, x0, c, d), cov_func=cov_base)
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-5)
X = np.linspace(0, 10, 400)[:, None]
lfunc = logistic(X.flatten(), a, b, c, d).eval()
plt.plot(X, lfunc)
plt.xlabel("X")
plt.ylabel(r"$\phi(x)$")
plt.title("The scaling function")
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
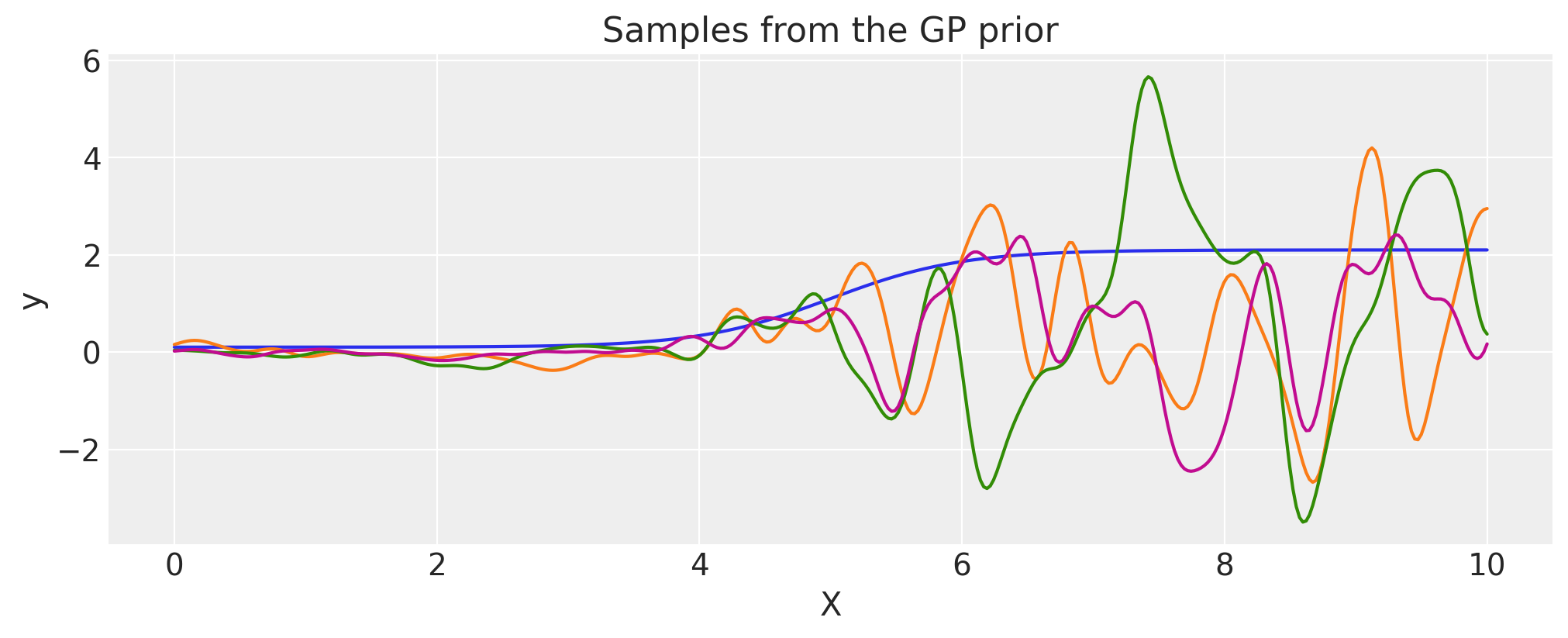
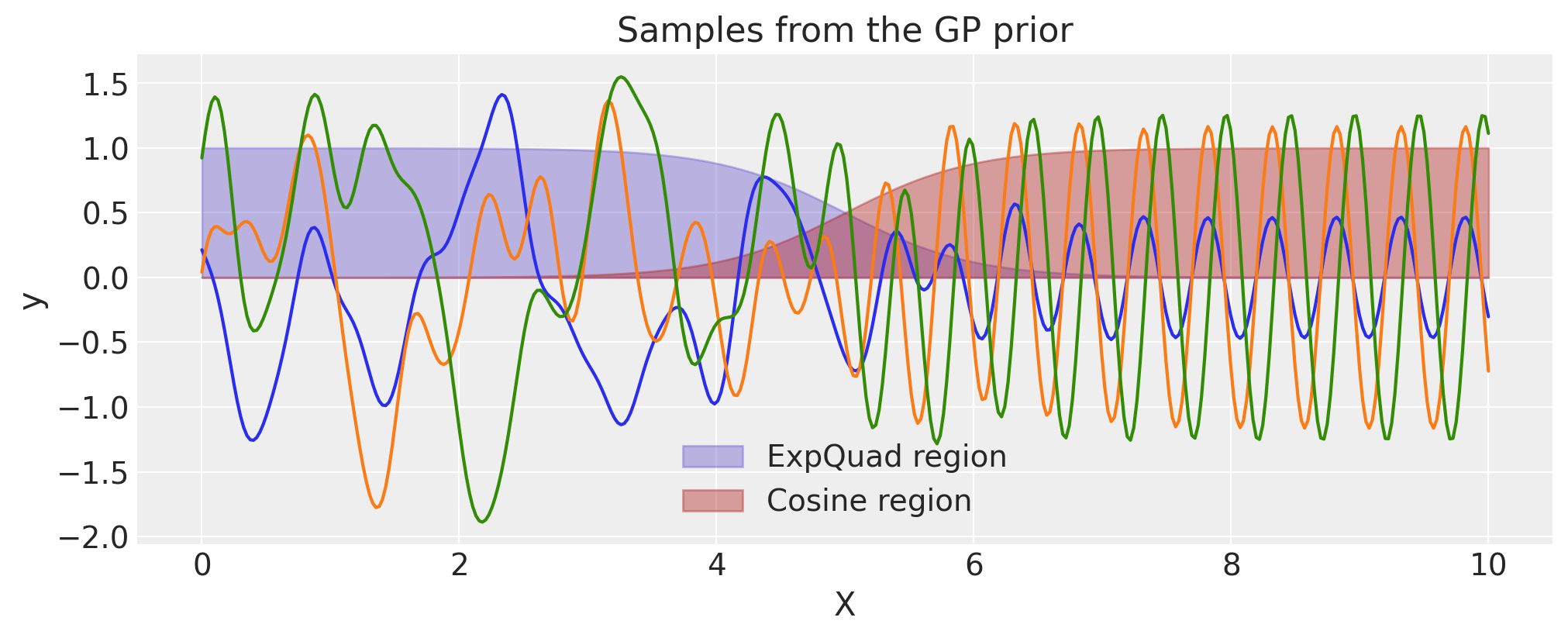
使用ScaledCov构建一个变化点核#
The ScaledCov 核函数可以用来创建 Changepoint 协方差。这种协方差模型描述了一个过程,该过程逐渐从一种行为类型过渡到另一种行为类型。
变化点核由以下公式给出
其中 \(\phi(x)\) 是逻辑函数。
def logistic(x, a, x0):
# a is the slope, x0 is the location
return pm.math.invlogit(a * (x - x0))
a = 2.0
x0 = 5.0
cov1 = pm.gp.cov.ScaledCov(
1, scaling_func=logistic, args=(-a, x0), cov_func=pm.gp.cov.ExpQuad(1, 0.2)
)
cov2 = pm.gp.cov.ScaledCov(
1, scaling_func=logistic, args=(a, x0), cov_func=pm.gp.cov.Cosine(1, 0.5)
)
cov = cov1 + cov2
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-5)
X = np.linspace(0, 10, 400)
plt.fill_between(
X,
np.zeros(400),
logistic(X, -a, x0).eval(),
label="ExpQuad region",
color="slateblue",
alpha=0.4,
)
plt.fill_between(
X, np.zeros(400), logistic(X, a, x0).eval(), label="Cosine region", color="firebrick", alpha=0.4
)
plt.legend()
plt.xlabel("X")
plt.ylabel(r"$\phi(x)$")
plt.title("The two scaling functions")
K = cov(X[:, None]).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
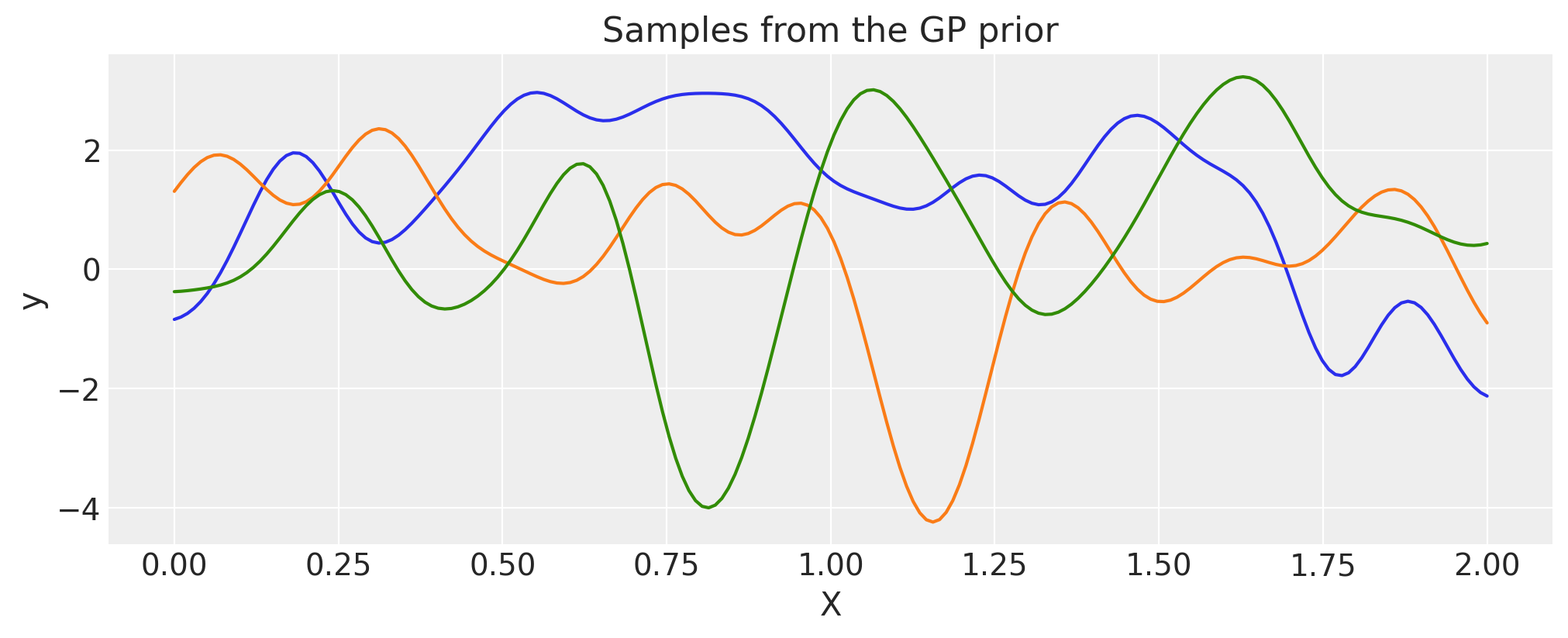
两个或多个协方差函数的组合#
您可以结合不同的协方差函数来建模复杂的数据。
特别是,您可以对任何协方差函数执行以下操作:
添加其他协方差函数,其维度与第一个协方差函数相等或可广播
与标量或具有相同或可广播维度的协方差函数相乘,并与第一个协方差函数结合
使用标量进行指数运算。
加法#
ls_1 = 0.1
tau_1 = 2.0
ls_2 = 0.5
tau_2 = 1.0
cov_1 = tau_1 * pm.gp.cov.ExpQuad(1, ls=ls_1)
cov_2 = tau_2 * pm.gp.cov.ExpQuad(1, ls=ls_2)
cov = cov_1 + cov_2
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
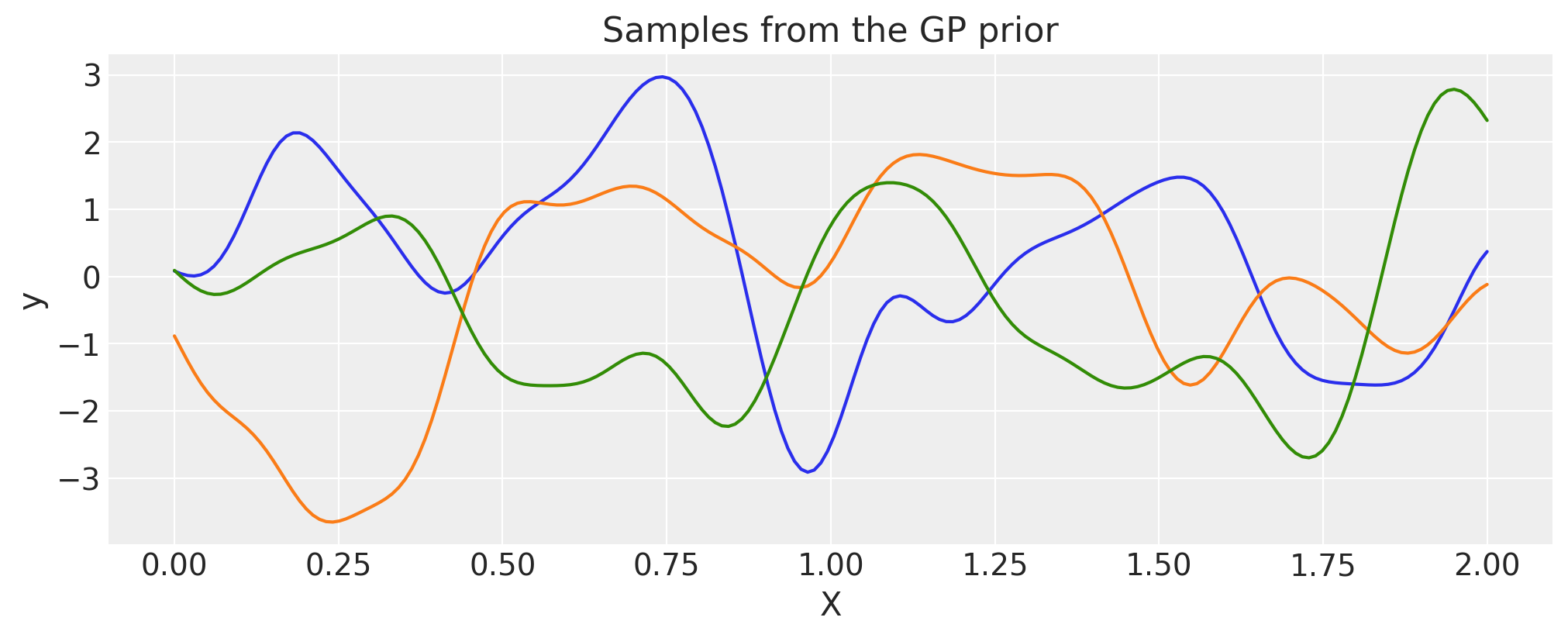
乘法#
ls_1 = 0.1
tau_1 = 2.0
ls_2 = 0.5
tau_2 = 1.0
cov_1 = tau_1 * pm.gp.cov.ExpQuad(1, ls=ls_1)
cov_2 = tau_2 * pm.gp.cov.ExpQuad(1, ls=ls_2)
cov = cov_1 * cov_2
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
指数运算#
ls_1 = 0.1
tau_1 = 2.0
power = 2
cov_1 = tau_1 * pm.gp.cov.ExpQuad(1, ls=ls_1)
cov = cov_1**power
# Add white noise to stabilise
cov += pm.gp.cov.WhiteNoise(1e-6)
X = np.linspace(0, 2, 200)[:, None]
K = cov(X).eval()
plt.plot(
X,
pm.draw(pm.MvNormal.dist(mu=np.zeros(len(K)), cov=K, shape=len(K)), draws=3, random_seed=rng).T,
)
plt.title("Samples from the GP prior")
plt.ylabel("y")
plt.xlabel("X");
定义自定义协方差函数#
PyMC中的协方差函数对象需要实现__init__、diag和full方法,并且是gp.cov.Covariance的子类。diag仅返回协方差矩阵的对角线,而full返回完整的协方差矩阵。full方法有两个输入X和Xs。full(X)返回方形的协方差矩阵,而full(X, Xs)返回两组输入之间的交叉协方差。
例如,这里是 WhiteNoise 协方差函数的实现:
class WhiteNoise(pm.gp.cov.Covariance):
def __init__(self, sigma):
super(WhiteNoise, self).__init__(1, None)
self.sigma = sigma
def diag(self, X):
return tt.alloc(tt.square(self.sigma), X.shape[0])
def full(self, X, Xs=None):
if Xs is None:
return tt.diag(self.diag(X))
else:
return tt.alloc(0.0, X.shape[0], Xs.shape[0])
如果我们遗漏了重要的协方差或均值函数,请随时提交拉取请求!
参考资料#
卡尔·爱德华·拉斯穆森和克里斯托弗·K.I.威廉姆斯。《高斯过程在机器学习中的应用》。麻省理工学院出版社,2006年。ISBN 026218253X。网址:https://gaussianprocess.org/gpml/。
Espéran Padonou 和 O Roustant。用于在圆形域上预测的极性高斯过程。工作论文或预印本,2015年2月。URL: https://hal.archives-ouvertes.fr/hal-01119942.
水印#
%load_ext watermark
%watermark -n -u -v -iv -w -p xarray
Last updated: Fri Nov 17 2023
Python implementation: CPython
Python version : 3.11.5
IPython version : 8.17.2
xarray: 2023.10.1
matplotlib: 3.8.1
arviz : 0.16.1
pymc : 5.9.2
pytensor : 2.17.4
numpy : 1.26.2
Watermark: 2.4.3